library(epifitter) # Para AUDPC(), cv.model(), e o dataset PowderyMildew
library(ggplot2) # Para visualizações com ggplot
library(dplyr) # Para filter(), group_by(), summarise(), pipe (%>%) ou |>
library(DHARMa) # Para simulate_residuals()
library(emmeans) # Para emmeans() e cld()
library(multcomp)audpc
AUDPC
Esse script em R realiza uma análise da severidade de oídio (um tipo de doença fúngica) em diferentes sistemas de irrigação e níveis de umidade, usando gráficos, cálculo da área abaixo da curva de progresso da doença (AUDPC), ANOVA e comparação de médias. Abaixo está a interpretação detalhada e explicativa de cada etapa e da tabela final:
library(epifitter)
oidio <- PowderyMildew
#Vários tipos de gráficos
oidio |>
ggplot(aes(factor (time), sev)) +
geom_jitter(width=0.1) +
facet_wrap(irrigation_type ~ moisture)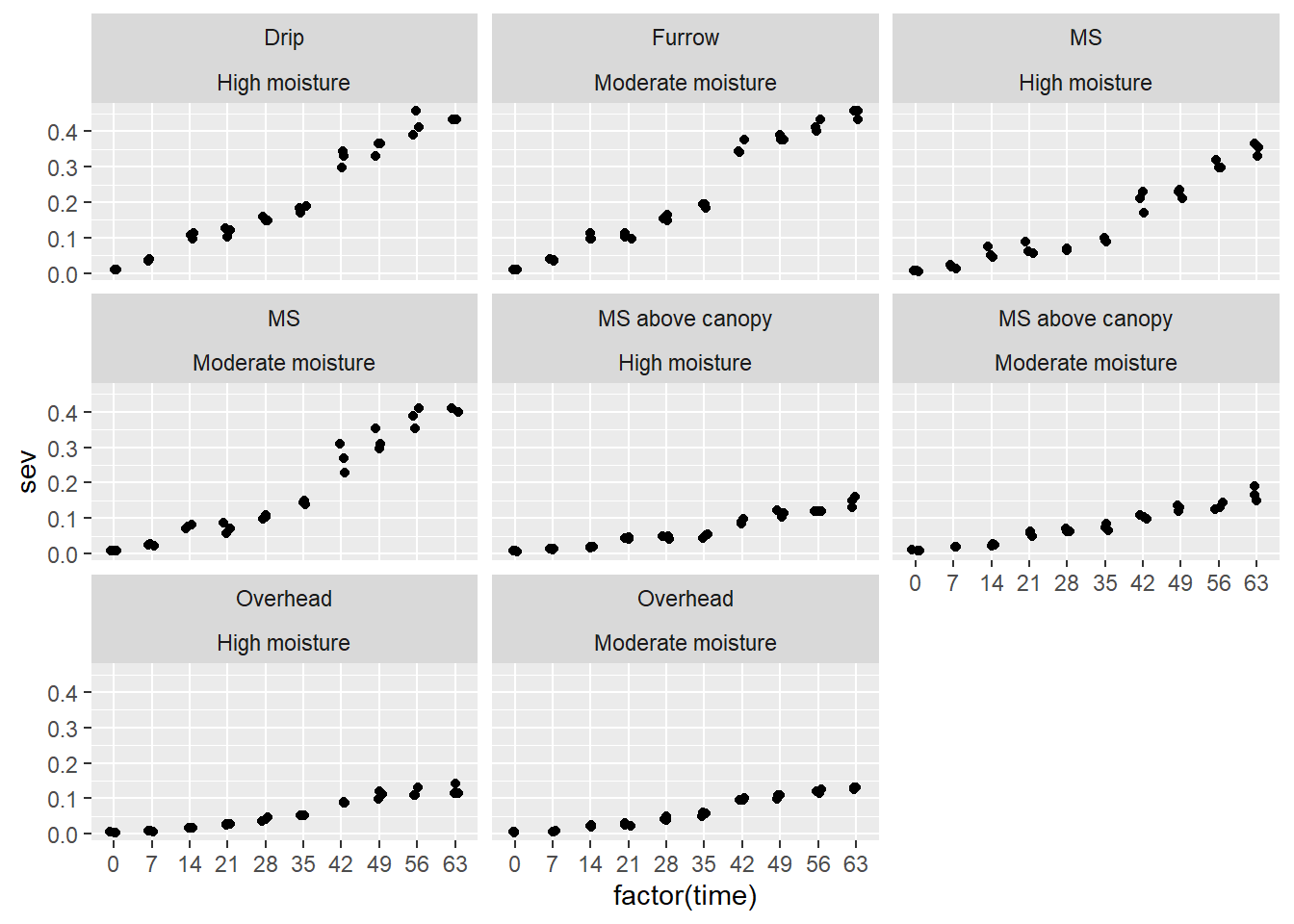
oidio |>
ggplot(aes(factor (time), sev)) +
geom_jitter(width=0.1) +
facet_grid(moisture ~ irrigation_type)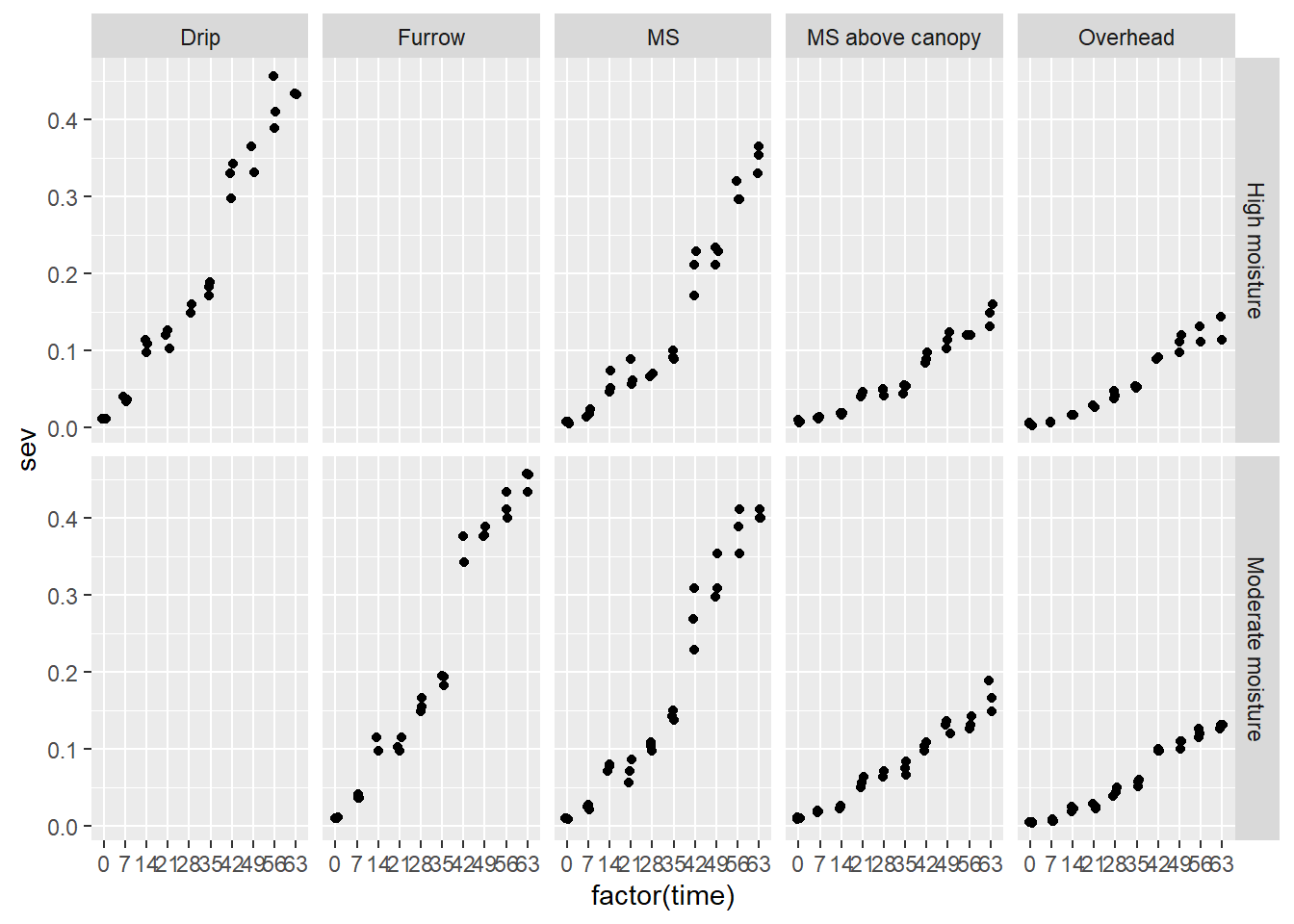
oidio2 <- oidio|>
filter(irrigation_type %in% c("MS", "MS above canopy", "Overhead"))
oidio2 |> ggplot(aes(time, sev)) +
geom_point() +
facet_grid(moisture ~ irrigation_type)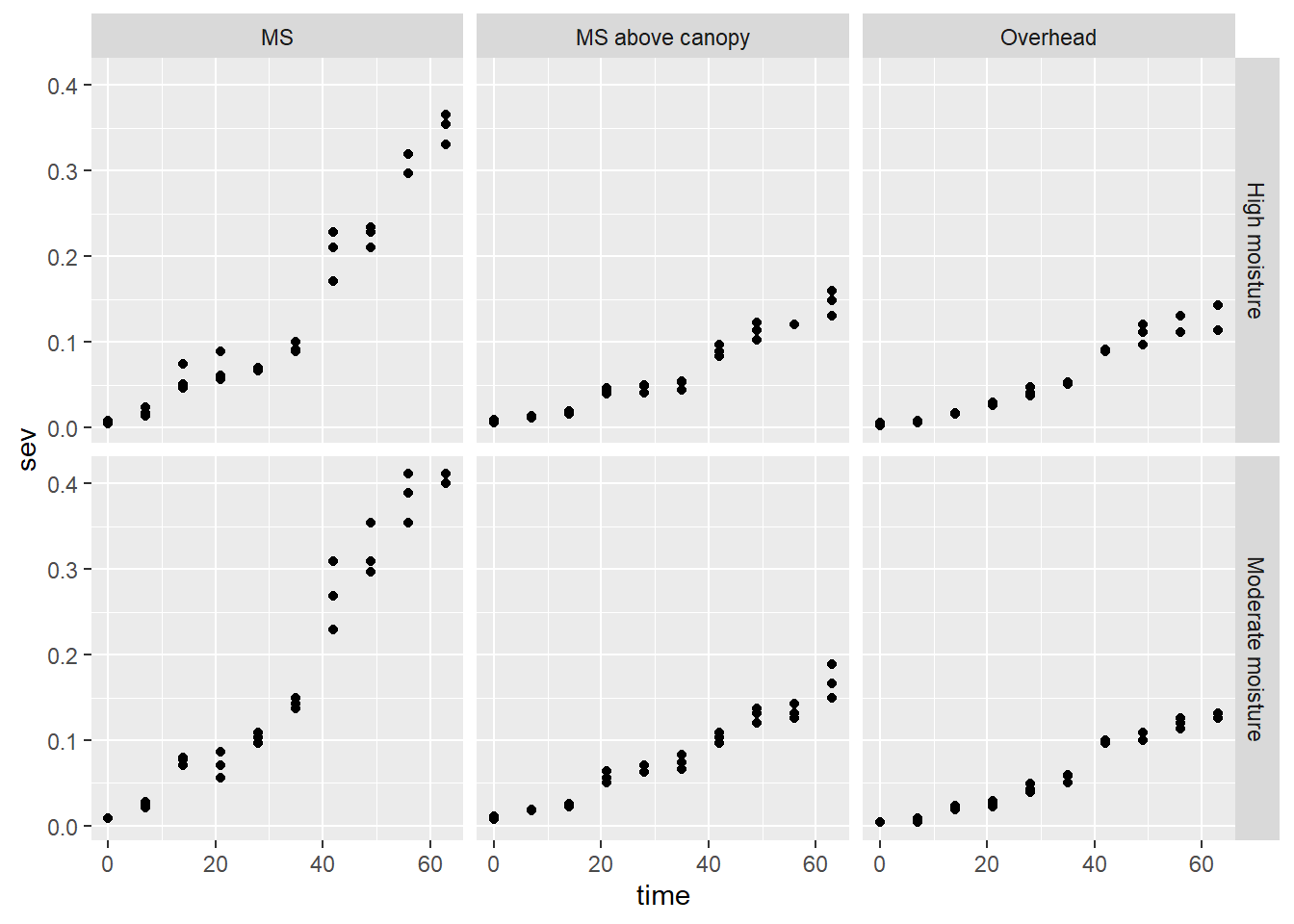
#Calcular média abaixo da curva
oidio3 <- oidio2 |>
group_by(irrigation_type, moisture, block) |>
summarise(AUDPC = AUDPC(time, sev))
#Plotar área abaixo da curva
oidio3 |>
ggplot(aes(irrigation_type, AUDPC, color = moisture)) +
geom_point(size = 2) +
scale_y_continuous(limits = c(0,20))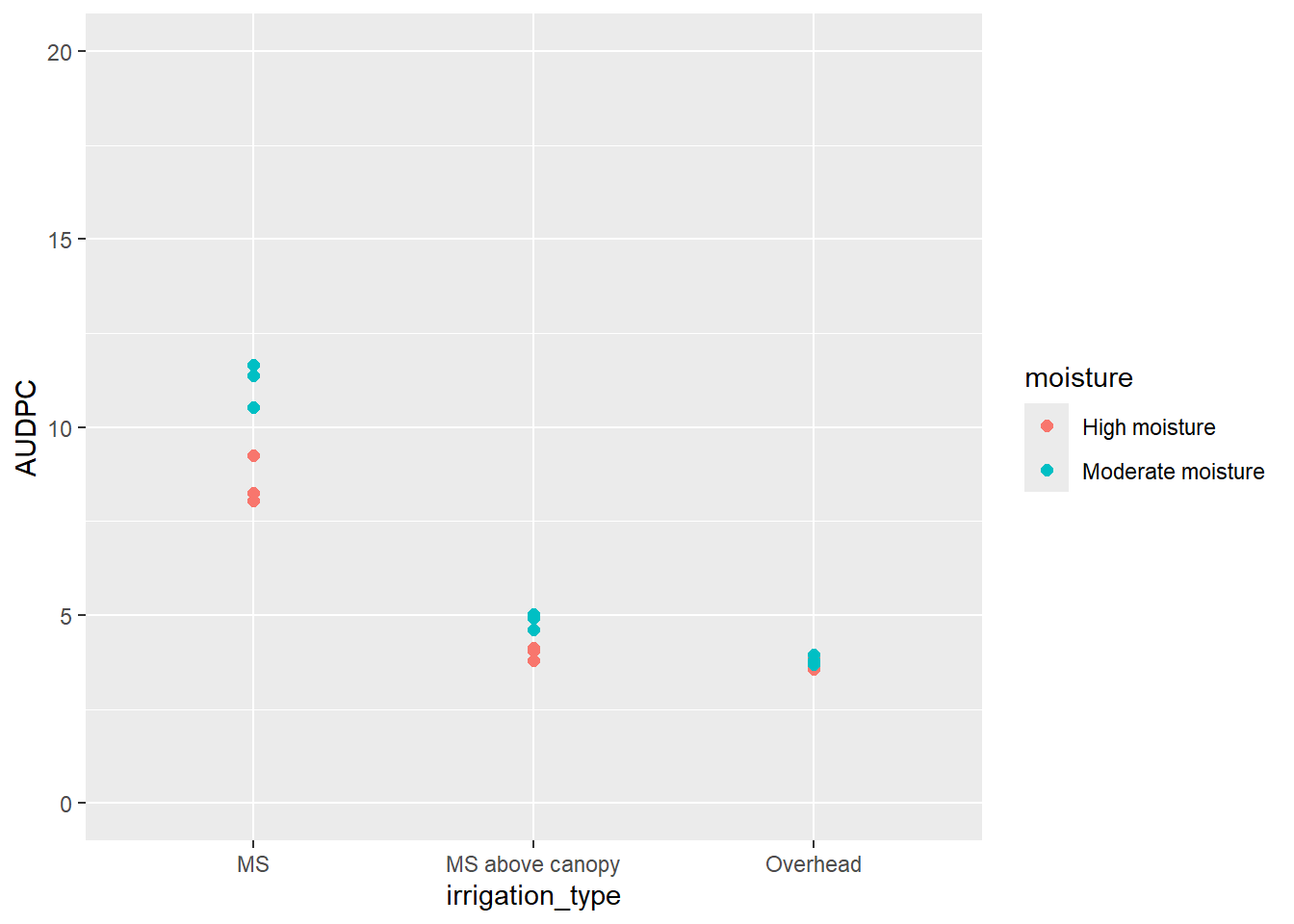
#Verificar se há diverenças
#Fazer ANOVA
oidio4 <- lm(AUDPC ~ irrigation_type*moisture, data = oidio3)
anova(oidio4)Analysis of Variance Table
Response: AUDPC
Df Sum Sq Mean Sq F value Pr(>F)
irrigation_type 2 134.341 67.170 451.721 5.073e-12 ***
moisture 1 6.680 6.680 44.924 2.188e-05 ***
irrigation_type:moisture 2 5.104 2.552 17.162 0.0003022 ***
Residuals 12 1.784 0.149
---
Signif. codes: 0 '***' 0.001 '**' 0.01 '*' 0.05 '.' 0.1 ' ' 1plot(simulateResiduals(oidio4))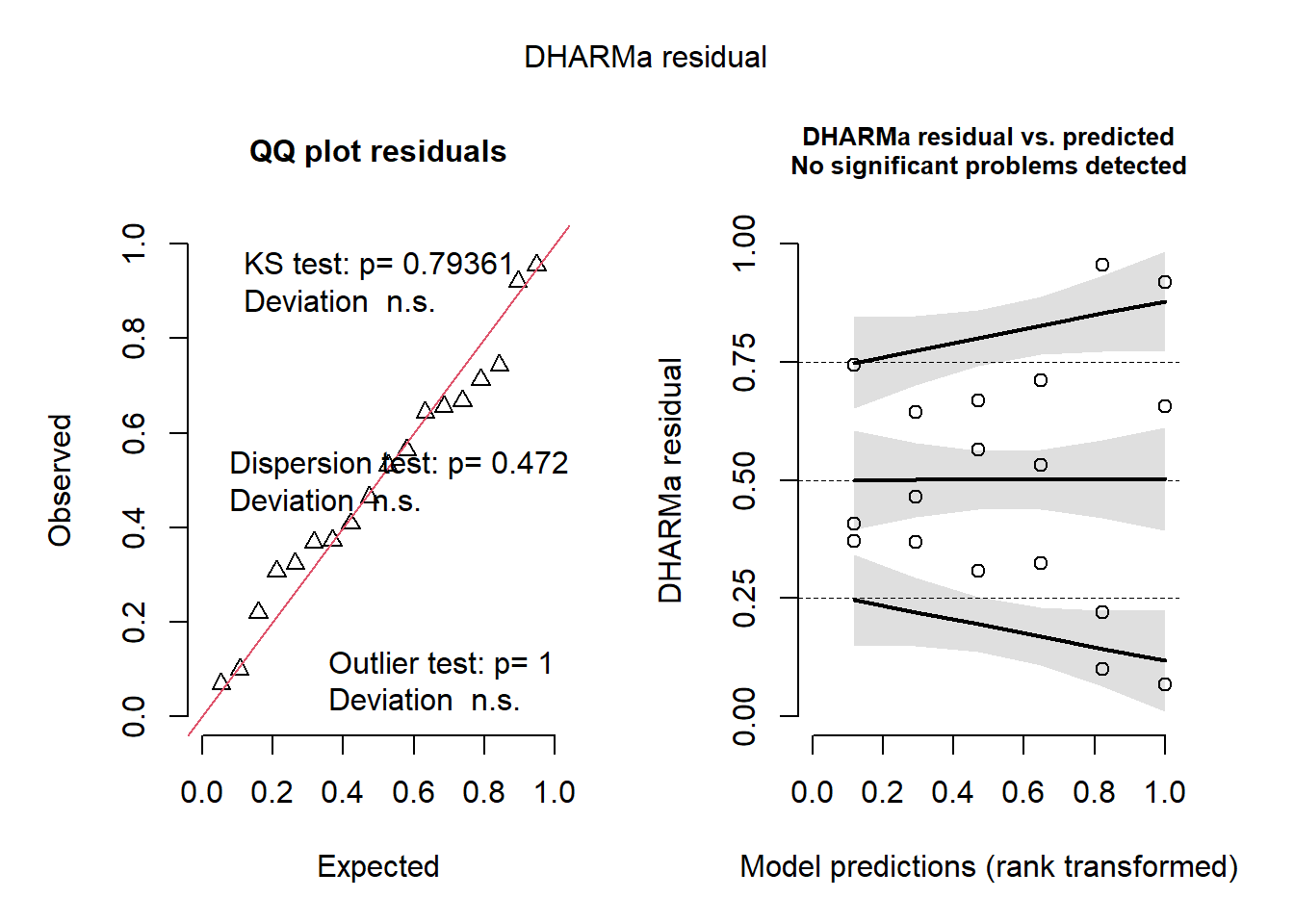
#Ver visualmente se é diferente
medias_oidio <- emmeans(oidio4, ~ moisture | irrigation_type)
cld(medias_oidio)irrigation_type = MS:
moisture emmean SE df lower.CL upper.CL .group
High moisture 8.52 0.223 12 8.04 9.01 1
Moderate moisture 11.18 0.223 12 10.70 11.67 2
irrigation_type = MS above canopy:
moisture emmean SE df lower.CL upper.CL .group
High moisture 3.99 0.223 12 3.51 4.48 1
Moderate moisture 4.86 0.223 12 4.37 5.34 2
irrigation_type = Overhead:
moisture emmean SE df lower.CL upper.CL .group
High moisture 3.68 0.223 12 3.20 4.17 1
Moderate moisture 3.81 0.223 12 3.33 4.30 1
Confidence level used: 0.95
significance level used: alpha = 0.05
NOTE: If two or more means share the same grouping symbol,
then we cannot show them to be different.
But we also did not show them to be the same. medias_oidio2 <- emmeans(oidio4, ~ irrigation_type | moisture)
cld(medias_oidio2)moisture = High moisture:
irrigation_type emmean SE df lower.CL upper.CL .group
Overhead 3.68 0.223 12 3.20 4.17 1
MS above canopy 3.99 0.223 12 3.51 4.48 1
MS 8.52 0.223 12 8.04 9.01 2
moisture = Moderate moisture:
irrigation_type emmean SE df lower.CL upper.CL .group
Overhead 3.81 0.223 12 3.33 4.30 1
MS above canopy 4.86 0.223 12 4.37 5.34 2
MS 11.18 0.223 12 10.70 11.67 3
Confidence level used: 0.95
P value adjustment: tukey method for comparing a family of 3 estimates
significance level used: alpha = 0.05
NOTE: If two or more means share the same grouping symbol,
then we cannot show them to be different.
But we also did not show them to be the same. residuosoidio4 <- residuals(oidio4)
sd_res <- sd(residuosoidio4)
media_fitted <- mean(fitted(oidio4))
cv <- (sd_res / media_fitted) * 100
print(cv)[1] 5.392371| H moisture | M moisture | |
|---|---|---|
| Irrigation | ||
| MS | 8,52 Aa | 11,18 Ab |
| MS AC | 3,99 Ba | 4,86 Bb |
| Overhead | 3,68 Ba | 3,81 Ca |
| CV = 5,39 |